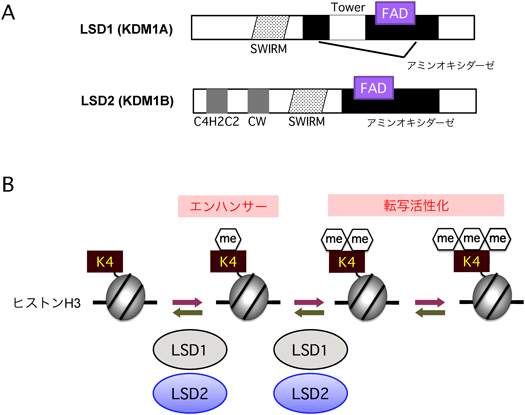
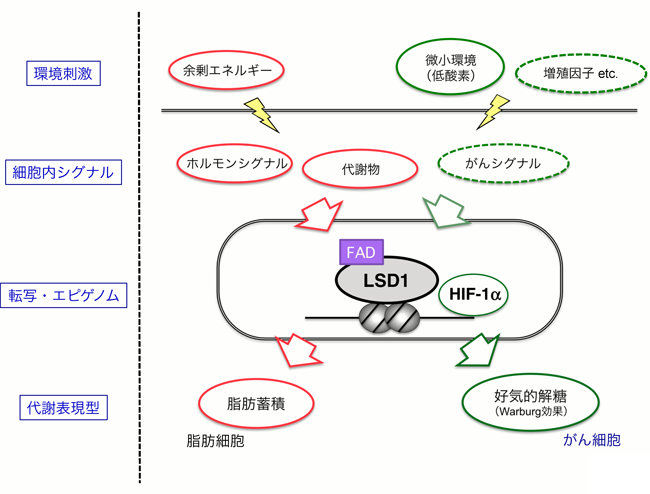
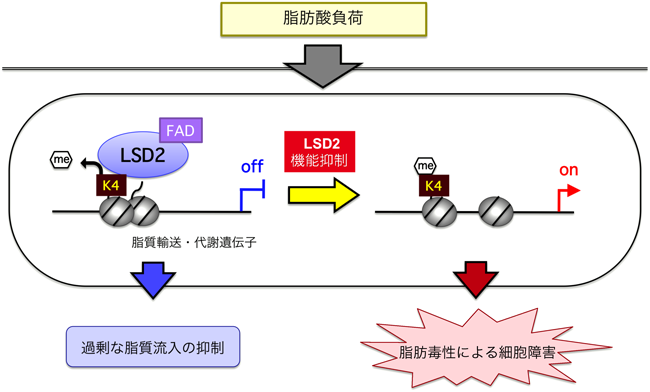
細胞内代謝とエピゲノム制御のクロストークMolecular mechanisms of metabolism-epigenome crosstalk
熊本大学発生医学研究所発生制御部門細胞医学分野Department of Medical Cell Biology, Division of Developmental Regulation, Institute of Molecular Embryology and Genetics, Kumamoto University ◇ 〒860-0811 熊本県熊本市中央区本荘二丁目2番1号Honjo 2-2-1, Chuo-ku, Kumamoto-shi, Kumamoto 860-0811, Japan