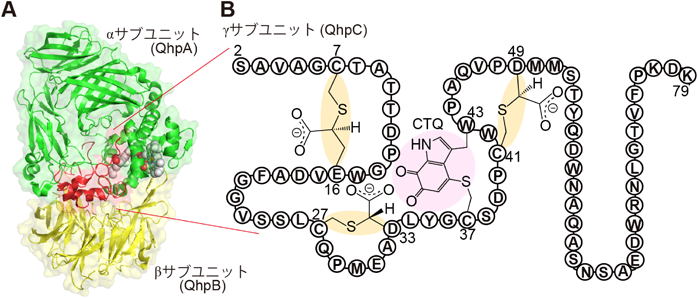
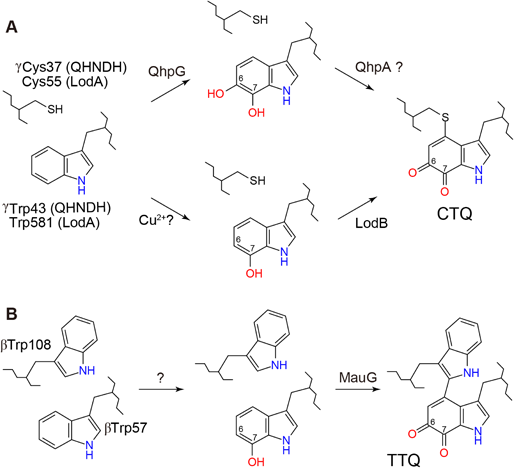
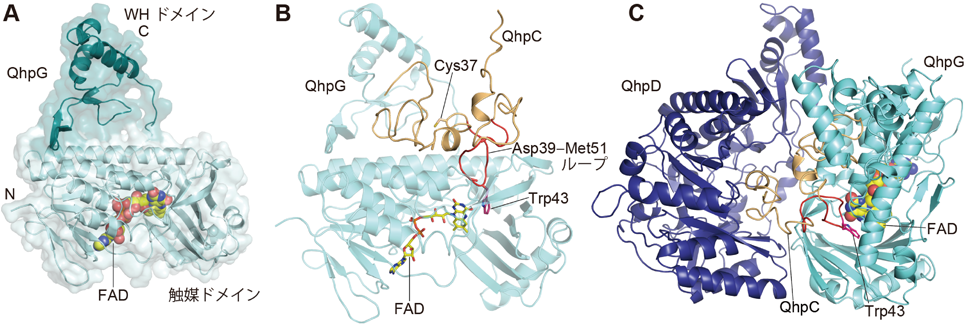
キノン補酵素形成に関わる新奇フラビン酵素の構造と機能Structure and function of a novel flavoenzyme involved in quinone cofactor biogenesis
1 広島工業大学生命学部食品生命科学科Graduate School of Science and Technology, Hiroshima Institute of Technology ◇ 〒731–5193 広島県広島市佐伯区三宅2–1–1 ◇ 2–1–1 Miyake, Saeki-ku, Hiroshima 731–5193, Japan
2 大阪大学産業科学研究所生体分子反応科学研究分野Department of Biomolecular Science and Reaction, Institute of Scientific and Industrial Research (SANKEN), Osaka University ◇ 〒567–0047 大阪府茨木市美穂ケ丘8–1 ◇ 8–1 Mihogaoka, Ibaraki, Osaka 567–0047, Japan